---
title: "Resumen de las observaciones de la iniciativa NeoMapas en iNaturalist"
author: "José R. Ferrer-Paris"
date: "2025-07-23"
date-modified: last-modified
categories: [R, rinat, Español, plotly, ggplot2, tmap, Venezuela]
output: html_document
editor_options:
chunk_output_type: console
execute:
echo: true
message: true
warning: true
format:
html:
code-tools:
source: true
caption: "Code for this document"
image: "https://inaturalist-open-data.s3.amazonaws.com/photos/2002533/medium.jpg"
image-alt: "(c) JR Ferrer-Paris, some rights reserved (CC BY)"
lang: es
---
En este documento muestro un resumen de las observaciones realizadas en iNaturalist durante mis años de trabajo en la iniciativa NeoMapas.
## Cargar paquetes
```{r setup}
library(ggplot2)
library(rinat)
library(dataverse)
library(tmap)
library(DT)
library(sf)
library(plotly)
library(stringr)
library(lubridate)
library(dplyr)
```
## Leer datos de iNaturalist
```{r}
here::i_am("projects/NeoMapas-dashboard.qmd")
if (!dir.exists(here::here("data")))
dir.create(here::here("data"))
inat_obs_data <- here::here("data", "inat-obs.rds")
if (file.exists(inat_obs_data)) {
user_obs <- readRDS(inat_obs_data)
} else {
user_obs <- get_inat_obs_user("NeoMapas",maxresults = 5000) |>
mutate(dts=date(datetime), year=year(dts), month=month(dts))
saveRDS(user_obs, inat_obs_data)
}
```
## Leer datos espaciales de la iniciativa NeoMapas
```{r}
dest_file <- tempfile(fileext=".gpkg")
binary_file <- get_file_by_name(filename="VBG.gpkg",dataset="10.7910/DVN/IME0M5")
writeBin(binary_file, dest_file)
CNEB <- read_sf(dest_file)
```
## Preparar los datos
```{r}
lookup <- c(name="scientific_name",
user="user_login",
#date="observed_on",
taxonid="id",
taxon="iconic_taxon_name",
kingdom="taxon_kingdom_name",
phylum="taxon_phylum_name",
class="taxon_class_name",
order="taxon_order_name",
genus="taxon_genus_name"
)
NeoMapas_obs <- user_obs |>
mutate(date=ymd(observed_on),
filter1 = grepl("Muestreos de NeoMapas", tag_list),
URA=str_extract(tag_list,"NM[0-9]+")) |>
rename(any_of(lookup)) |>
filter(
latitude > 0 &
latitude <13 &
longitude < -60 &
longitude > -80) |>
filter(filter1 | year(date) %in% 2003:2012) |>
st_as_sf(coords=c("longitude","latitude"), crs=4326)
```
```{r}
qry <- st_intersects(NeoMapas_obs,CNEB)
NeoMapas_obs[lengths(qry)==1,"CN"] <- {CNEB |> slice(unlist(qry)) |> pull(cdg)}
NeoMapas_obs <- NeoMapas_obs |>
mutate(unidad=case_when(
!is.na(URA) & !is.na(CN) ~ sprintf("%s (%s)",URA,CN),
!is.na(CN) ~ sprintf("celda %s",CN),
TRUE ~ "sin información"))
obs_byyear <- as.data.frame(table(year(NeoMapas_obs$date)))
colnames(obs_byyear) <- c("Año","Observaciones")
```
## Dimensión espacial
### Unidades regionales de NeoMapas
```{r uralist}
NeoMapas_obs |>
st_drop_geometry() |>
group_by("Unidades regionales"=unidad) |>
summarise(Observaciones=n_distinct(date), Registros=n()) |>
arrange(desc(Observaciones)) |>
DT::datatable(style="bootstrap")
```
### Lugares
```{r sitelist}
NeoMapas_obs |>
st_drop_geometry() |>
group_by("Lugar"=place_guess) |>
summarise(Observaciones=n_distinct(date), Registros=n()) |>
arrange(desc(Observaciones)) |>
DT::datatable(style="bootstrap")
```
### Mapa
```{r map, eval = TRUE}
popup_html <- with(NeoMapas_obs,
sprintf("<p><b>%s</b><br/><i>%s</i></p>
<p>Observada en <u>%s</u> el %s<br/>
<p>
<img src='%s' width='200'/><br/>
<a href='%s' target='inat'>Ver en iNaturalist</a>
</p>",
common_name, name, unidad,
date, image_url,url))
#tmap_mode("view")
CNEB_slc <- CNEB |>
filter(UM>0) |>
select(celda=cdg)
map1 <- tm_shape(CNEB_slc) +
tm_polygons(fill_alpha=.33) +
tm_minimap()
tmap_leaflet(map1) |> leaflet::addMarkers(data = NeoMapas_obs,
popup = ~popup_html)
```
## Dimensión taxonómica
### Observaciones por Phylum
```{r donut}
taxranks = as.data.frame(table(NeoMapas_obs$taxon))
p = taxranks |> plot_ly(labels = ~Var1, values=~Freq) |>
add_pie(hole=0.6) |>
layout(title = ~paste0("Numero total de Taxa: ", length(unique(NeoMapas_obs$taxonid))))
plotly::config(p,displayModeBar = F)
```
### Especies
```{r taxalist}
NeoMapas_obs |>
st_drop_geometry() |>
group_by("Especies"=name) |>
summarise(Observaciones=n_distinct(date), Registros=n()) |>
arrange(desc(Observaciones)) |>
DT::datatable(style="bootstrap")
```
## Observaciones en el tiempo
### Observaciones por año
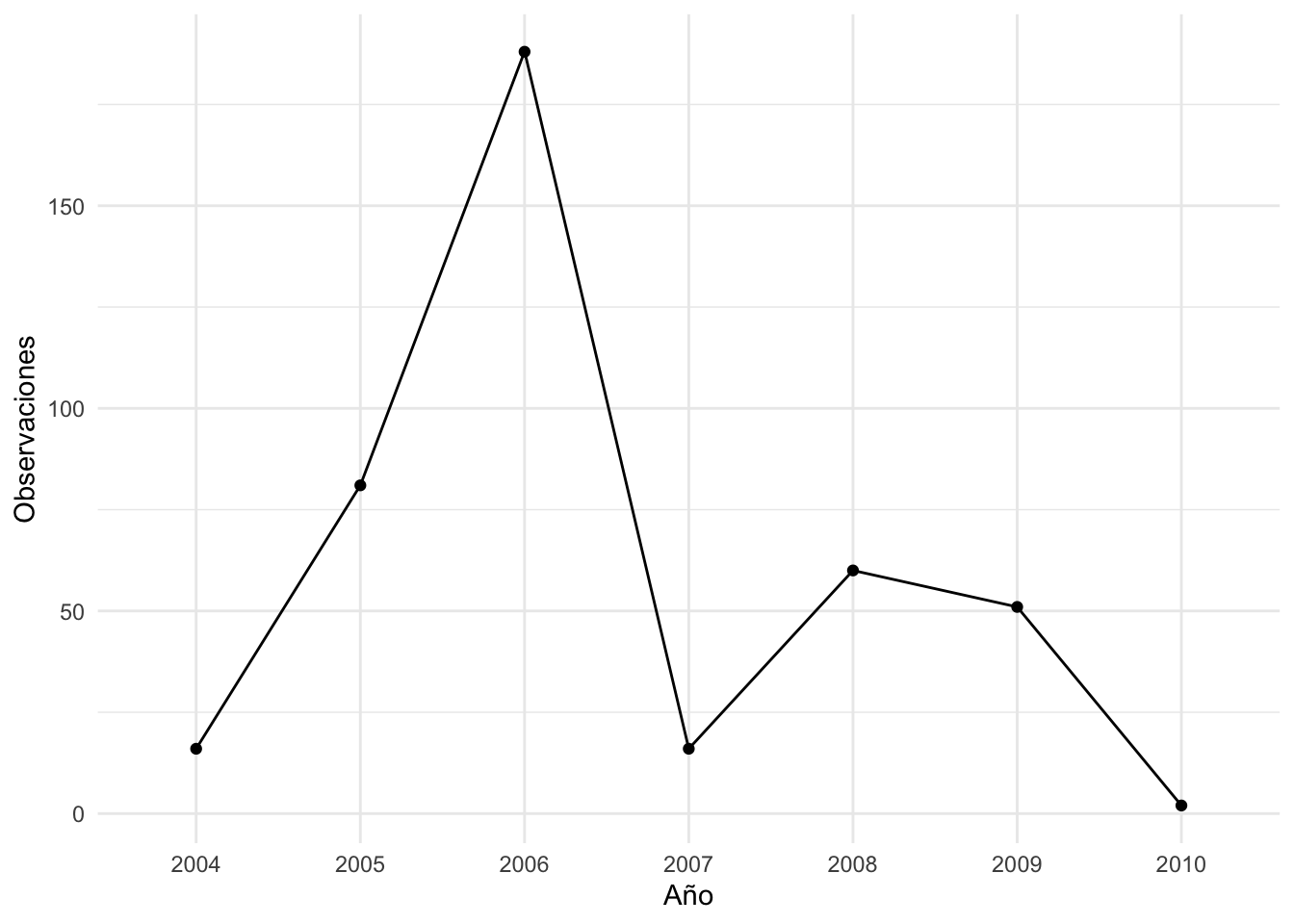
```{r obsbyyear}
#plot number of observation by date
ggplot(obs_byyear, aes(x=Año,y=Observaciones,group=1)) + geom_line() + geom_point()+ xlab("Año") + ylab("Observaciones") + theme_minimal()
```
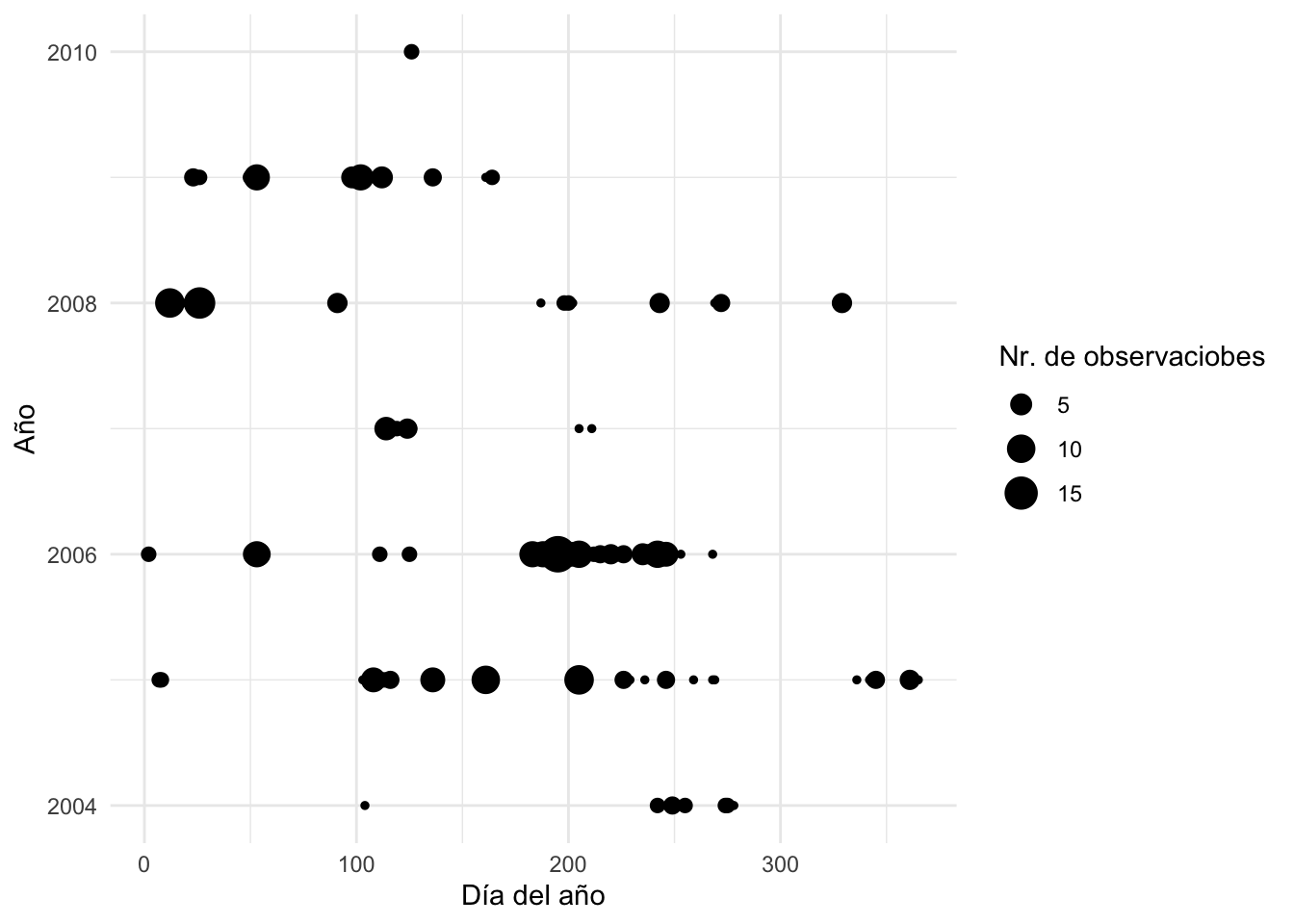
### Calendario de observaciones
```{r calobs2022}
inat_obs_day <- NeoMapas_obs |>
transmute(obs_year=year(date),
obs_day=yday(date)) |>
group_by(obs_year,obs_day,.groups = "drop") |>
summarise(Freq=n()) |>
mutate(obs_day=as.numeric(as.character(obs_day)))
ggplot(inat_obs_day,aes(x=obs_day,y=obs_year,size=Freq)) +
geom_point() +
labs(x="Día del año",
y="Año",
size = "Nr. de observaciobes") +
theme_minimal()
```